Wissenschaftliche Daten zu publizieren ist das Ziel eines jeden akademischen Forschungsprojektes. Leider kommt das nur relativ selten vor. Es dauert eben seine Zeit, bis die Experimente geplant und durchgeführt, die Daten analysiert, das Manuskript geschrieben, eingereicht und akzeptiert ist. Insofern ist das, was mir in den letzten drei Wochen widerfahren ist durchaus Grund zum Feiern: Ich habe drei Papers publiziert.
Zum Glück sind alle drei Veröffentlichungen thematisch verwandt, so dass ich sie hier in einem Blogpost vorstellen kann. Ganz allgemein geht es darum, biologisch relevante Schlussfolgerungen aus den großen Datensätzen zu ziehen. Big Data in der Biologie.
In den letzten Jahren haben sich die High-Throughput Analysemethoden in der Molekularbiologie ständig verbessert, so dass inzwischen mit relativ wenig Aufwand, große Datensätze durch die Analyse komplexer Proben gewonnen werden können. Omics ist der Modebegriff, der dabei auf alles angewendet wird, was nicht direkt an einer Hand abzuzählen ist. Also: Genomics für mRNA Analysen, Proteomics für die Analyse komplexer Proteinproben, und Metabolomics für, leicht zu erraten, die großflächige Untersuchung der zellulären Metabolite. Diese Omics Begriffe werden wirklich inflationär benutzt. Auf Wikipedia existiert sogar eine Liste mit ein paar Dutzend dieser mehr oder weniger populären Omics Begriffe.
Leider reicht es häufig nicht mehr aus zu sagen was in einer biologischen Probe drin ist und einfach eine Liste der identifizierten zellulären Bestandteile zu publizieren. Inzwischen sind quantitative, vergleichende Analysen gefragt, um beispielsweise ein und denselben Bakterienstamm mit und ohne bestimmte Mutationen zu untersuchen. Diesen Ansatz haben wir in dem Borras et al. Paper gewählt. Wie verändert sich das Proteom von Mycoplasma pneumoniae wenn wichtige Gene ausgeknockt werden? Es kommt auf das Gen an, und auf die Analysemethode.
Für das Wodke et al. Paper haben wir ein Modell des gesamten Zellmetabolismus von M. pneumoniae mit quantitativen, experimentellen Daten abgeglichen und dabei eine erstaunliche Entdeckung gemacht: Das Bakterium nutzt die ihm zur Verfügung stehende Energie nur sehr ineffizient für Wachstum. Ein Großteil der Energie entfällt auf einfache Instandhaltungsreaktionen, wie beispielsweise die Regulierung des intrazellulären pHs.
Außerdem zeigen wir in dem Paper, dass wir durch das Verknüpfen der Parametersätze an unterschiedlichen Zeitpunkten entlang der Wachstumskurve von M. pneumoniae aus einem statischen Modell ein quasidynamisches Modell generieren können. Dieser Ansatz vereinfacht die Modellierung komplexer biologischer Vorgänge ungemein, da dynamische Modelle zwar genauer sein können, jedoch mit zunehmender Komplexität schnell unlösbar werden. Unser Modell ist so gut, dass wir damit vorhersagen können, was passiert wenn einzelne Gene oder Kombinationen aus zwei Genen ausgeknockt werden.
Für das dritte Paper haben wir erst die Metabolite in M. pneumoniae gemessen, und wo technisch möglich quantifiziert, und dann diese Ergebnisse mit Proteomics- und Genomics-Ergebnissen verbunden. Dank dieses neuen, integrativen Ansatzes können wir erklären, wie M. pneumoniae mit den zu Verfügung stehenden Aminosäuren und Nukleobasen haushaltet. Wir haben sozusagen Angebot und Nachfrage von grundsätzlichen zellulären Bausteinen untersucht.
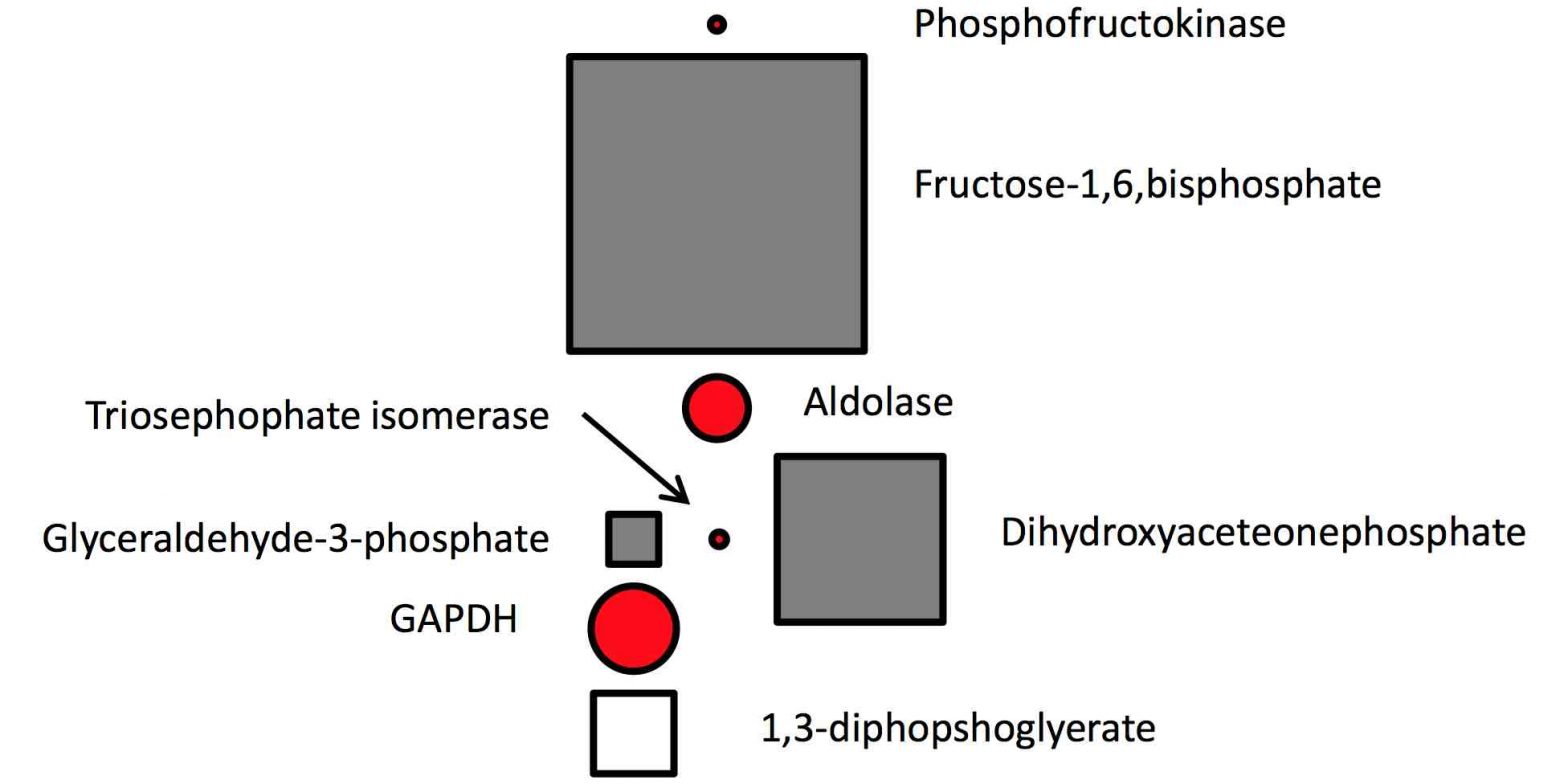
M. pneumoniae ist ein sehr einfaches Bakterium mit nicht einmal 700 Genen – ein Grund, warum wir es als Modellorganismus verwenden. Das Bakterium hat dementsprechend auch einen sehr einfachen Stoffwechsel. Es nimmt Glucose als Energiequelle auf, metabolisiert diese zu Pyruvat in der Glyolyse und sekretiert schließlich Milch- und Essigsäure. Mit Hilfe von Enzymassays können wir die Geschwindigkeit messen, mit der M. pneumoniae die Glucose metabolisiert.
Durch die quantitative Bestimmung der intrazellulären Glycolyseintermediate und der bei deren Umsetzung beteiligten Enzyme des zellulären Energiestoffwechsels, können wir nach Integration mit der Geschwindigkeit, in der die Glucose metabolisiert wird, die intrazelluläre Aktivität der Glycolyseenzyme abschätzen. Biochemiker machen das in vitro mit aufgereinigten Komponenten, wir haben versucht, einen Eindruck von der Enzymaktivität direkt in der Zelle zu bekommen.
Soweit ein kurzer Abriss der Inhalte der drei Publikationen. Natürlich habe ich das nicht alles alleine erforscht, und ich schreibe ja auch schon die ganze Zeit von „wir„. In den Papers steht detailliert wer wie und was beigetragen hat, namentlich möchte ich hier dennoch Judith Wodke erwähnen, die ich die letzten Jahre als Doktorandin betreut habe und die jetzt wieder in Berlin ist. Mit Ricardo Gutierrez und Josep Marcos habe ich seit Jahren zur quantitativen Messung intrazellulärer Metabolite kooperiert. Beide sind sonst mit der Untersuchung von Dopingproben beschäftigt. Großer Dank gilt natürlich auch allen anderen Autoren, insbesondere Manuel Liebeke, Edda Klipp und Luis Serrano.
Heute Nachmittag feiern wir die Papers. Traditionell mit Cava, Pan con Tomate, Queso und Jamon auf der Terrasse meines – jetzt ehemaligen – Institutes. Außerdem ist heute noch Sant Jordi und heute Abend spielt Bayern gegen Barça. Ich habe das Gefühl, es wird ein langer Tag – und eine lange Nacht.
 Wodke, J., Puchałka, J., Lluch-Senar, M., Marcos, J., Yus, E., Godinho, M., Gutiérrez-Gallego, R., dos Santos, V., Serrano, L., Klipp, E., & Maier, T. (2013). Dissecting the energy metabolism in Mycoplasma pneumoniae through genome-scale metabolic modeling Molecular Systems Biology, 9 DOI: 10.1038/msb.2013.6
Wodke, J., Puchałka, J., Lluch-Senar, M., Marcos, J., Yus, E., Godinho, M., Gutiérrez-Gallego, R., dos Santos, V., Serrano, L., Klipp, E., & Maier, T. (2013). Dissecting the energy metabolism in Mycoplasma pneumoniae through genome-scale metabolic modeling Molecular Systems Biology, 9 DOI: 10.1038/msb.2013.6
 Borràs, E., Espadas, G., Mancuso, F., Maier, T., Chiva, C., & Sabidó, E. (2013). Integrative quantitation enables a comprehensive proteome comparison of two Mycoplasma pneumoniae genetic perturbations Molecular BioSystems DOI: 10.1039/C3MB25581F
Borràs, E., Espadas, G., Mancuso, F., Maier, T., Chiva, C., & Sabidó, E. (2013). Integrative quantitation enables a comprehensive proteome comparison of two Mycoplasma pneumoniae genetic perturbations Molecular BioSystems DOI: 10.1039/C3MB25581F
 Maier, T., Marcos, J., Wodke, J., Paetzold, B., Liebeke, M., Gutiérrez-Gallego, R., & Serrano, L. (2013). Large-scale metabolome analysis and quantitative integration with genomics and proteomics data in Mycoplasma pneumoniae Molecular BioSystems DOI: 10.1039/C3MB70113A
Maier, T., Marcos, J., Wodke, J., Paetzold, B., Liebeke, M., Gutiérrez-Gallego, R., & Serrano, L. (2013). Large-scale metabolome analysis and quantitative integration with genomics and proteomics data in Mycoplasma pneumoniae Molecular BioSystems DOI: 10.1039/C3MB70113A
Verwandte Artikel im Blog:
![]() Ingalhalikar M, Smith A, Parker D, Satterthwaite TD, Elliott MA, Ruparel K, Hakonarson H, Gur RE, Gur RC, & Verma R (2013). Sex differences in the structural connectome of the human brain. Proceedings of the National Academy of Sciences of the United States of America PMID: 24297904
Ingalhalikar M, Smith A, Parker D, Satterthwaite TD, Elliott MA, Ruparel K, Hakonarson H, Gur RE, Gur RC, & Verma R (2013). Sex differences in the structural connectome of the human brain. Proceedings of the National Academy of Sciences of the United States of America PMID: 24297904